жӮЁеҘҪпјҢзҷ»еҪ•еҗҺжүҚиғҪдёӢи®ўеҚ•е“ҰпјҒ
иҝҷзҜҮж–Үз« дё»иҰҒд»Ӣз»ҚдәҶGWASе“Ҳжё©е№іиЎЎжЈҖйӘҢзҡ„ж–№жі•зҡ„зӣёе…ізҹҘиҜҶпјҢеҶ…е®№иҜҰз»Ҷжҳ“жҮӮпјҢж“ҚдҪңз®ҖеҚ•еҝ«жҚ·пјҢе…·жңүдёҖе®ҡеҖҹйүҙд»·еҖјпјҢзӣёдҝЎеӨ§е®¶йҳ…иҜ»е®ҢиҝҷзҜҮGWASе“Ҳжё©е№іиЎЎжЈҖйӘҢзҡ„ж–№жі•ж–Үз« йғҪдјҡжңүжүҖ收иҺ·пјҢдёӢйқўжҲ‘们дёҖиө·жқҘзңӢзңӢеҗ§гҖӮ
гҖҢд»Җд№ҲжҳҜе“Ҳжё©е№іиЎЎпјҹгҖҚ
вққе“ҲиҝӘ-жё©дјҜж ј(Hardy-Weinberg)жі•еҲҷ е“ҲиҝӘ-жё©дјҜж јпјҲHardy-Weinbergпјүжі•еҲҷжҳҜзҫӨдҪ“йҒ—дј дёӯжңҖйҮҚиҰҒзҡ„еҺҹзҗҶпјҢе®ғи§ЈйҮҠдәҶз№Ғж®–еҰӮдҪ•еҪұе“ҚзҫӨдҪ“зҡ„еҹәеӣ е’Ңеҹәеӣ еһӢйў‘зҺҮгҖӮиҝҷдёӘжі•еҲҷжҳҜз”ЁHardy,G.H (иӢұеӣҪж•°еӯҰ家) е’ҢWeinbergпјҢW.пјҲеҫ·еӣҪеҢ»з”ҹпјүдёӨдҪҚеӯҰиҖ…зҡ„姓жқҘе‘ҪеҗҚзҡ„пјҢ他们дәҺеҗҢдёҖе№ҙпјҲ1908е№ҙпјүеҗ„иҮӘеҸ‘зҺ°дәҶиҝҷдёҖжі•еҲҷгҖӮ他们жҸҗеҮәеңЁдёҖдёӘдёҚеҸ‘з”ҹзӘҒеҸҳгҖҒиҝҒ移е’ҢйҖүжӢ©зҡ„ж— йҷҗеӨ§зҡ„йҡҸжңәдәӨй…Қзҡ„зҫӨдҪ“дёӯпјҢеҹәеӣ йў‘зҺҮе’Ңеҹәеӣ еһӢйў‘зҺҮе°ҶйҖҗд»ЈдҝқжҢҒдёҚеҸҳгҖӮ---зҷҫеәҰзҷҫ科
вқһ
гҖҢжҖҺд№ҲеҒҡе“Ҳжё©е№іиЎЎжЈҖйӘҢпјҹгҖҚ
вққгҖҢеҚЎж–№йҖӮеҗҲжҖ§жЈҖйӘҢпјҒгҖҚ пјҢдёҖдёӘзҫӨдҪ“жҳҜеҗҰз¬ҰеҗҲиҝҷз§ҚзҠ¶еҶөпјҢеҚіиҫҫеҲ°дәҶйҒ—дј е№іиЎЎпјҢд№ҹе°ұжҳҜдёҖеҜ№зӯүдҪҚеҹәеӣ зҡ„3з§Қеҹәеӣ еһӢзҡ„жҜ”дҫӢеҲҶеёғз¬ҰеҗҲе…¬ејҸпјҡp2+2pq+q2=1,p+q=1,(p+q)2=1.еҹәеӣ еһӢMMзҡ„йў‘зҺҮдёәp2,NNзҡ„йў‘зҺҮдёәq2,MNзҡ„йў‘зҺҮдёә2pqгҖӮMN:MNпјҡNNпјқP2пјҡ2pqпјҡq2гҖӮMNиҝҷеҜ№еҹәеӣ еңЁзҫӨдҪ“дёӯиҫҫжӯӨзҠ¶жҖҒпјҢе°ұжҳҜиҫҫеҲ°дәҶйҒ—дј е№іиЎЎгҖӮеҰӮжһңжІЎжңүиҫҫеҲ°иҝҷдёӘзҠ¶жҖҒпјҢе°ұжҳҜдёҖдёӘйҒ—дј дёҚе№іиЎЎзҡ„зҫӨдҪ“гҖӮдҪҶйҡҸзқҖзҫӨдҪ“дёӯзҡ„йҡҸжңәдәӨй…ҚпјҢе°ҶдјҡдҝқжҢҒиҝҷдёӘеҹәеӣ йў‘зҺҮе’Ңеҹәеӣ еһӢеҲҶеёғжҜ”дҫӢпјҢиҖҢиҫғжҳ“иҫҫеҲ°йҒ—дј е№іиЎЎзҠ¶жҖҒгҖӮеә”з”ЁHardy-WeinbergйҒ—дј е№іиЎЎеҗ»еҗҲеәҰжЈҖйӘҢж–№жі•пјҢжҠҠи®Ўз®—еҫ—еҲ°зҡ„еҹәеӣ йў‘зҺҮд»Је…ҘпјҢи®Ўз®—еҹәеӣ еһӢе№іиЎЎйў‘зҺҮпјҢеҶҚд№ҳд»ҘжҖ»дәәж•°пјҢжұӮеҫ—йў„жңҹеҖјпјҲeпјүгҖӮжҠҠи§ӮеҜҹж•°пјҲOпјүдёҺйў„жңҹеҖјпјҲeпјүдҪңжҜ”иҫғпјҢиҝӣиЎҢПҮ2жЈҖйӘҢгҖӮз—…дҫӢз»„е’ҢеҜ№з…§з»„зҡ„еҹәеӣ еһӢеҲҶеёғзҡ„и§ӮеҜҹеҖје’Ңйў„жңҹеҖје·®ејӮж— жҳҫи‘—жҖ§пјҲP>0.05пјүпјҢз¬ҰеҗҲйҒ—дј е№іиЎЎе®ҡеҫӢ.
вқһ
гҖҢе“Ҳжё©е№іиЎЎиҝҮж»Өе’ҢMAFиҝҮж»Өзҡ„еҢәеҲ«пјҹгҖҚ
вққд№ӢеүҚпјҢжҲ‘еҜ№иҝҷдёӨдёӘжҰӮеҝөжңүзӮ№ж··ж·ҶпјҢеҗҺжқҘжҳҺзҷҪиҝҮжқҘдәҶгҖӮиҝҷдёӨдёӘжҰӮеҝөдёҖдёӘжҳҜеҜ№еҹәеӣ йў‘зҺҮиҝӣиЎҢзҡ„зӯӣйҖүпјҢдёҖдёӘжҳҜеҜ№еҹәеӣ еһӢйў‘зҺҮиҝӣиЎҢзҡ„зӯӣйҖүгҖӮеҜ№дәҺдёҖдёӘдҪҚзӮ№вҖңAA AT TTвҖқпјҢе…¶дёӯAзҡ„йў‘зҺҮдёәеҹәеӣ йў‘зҺҮпјҢAAдёәеҹәеӣ еһӢйў‘зҺҮгҖӮMAFзӣҙжҺҘжҳҜеҜ№еҹәеӣ йў‘зҺҮиҝӣиЎҢзӯӣйҖүпјҢиҖҢе“Ҳжё©е№іиЎЎжЈҖйӘҢпјҢеҲҷжҳҜж №жҚ®еҹәеӣ еһӢжҺЁж–ӯеҮәзҗҶжғізҡ„пјҲAAпјҢATпјҢTTпјүзҡ„еҲҶеёғпјҢ然еҗҺе’Ңе®һйҷ…и§ӮеҜҹзҡ„иҝӣиЎҢйҖӮеҗҲжҖ§жЈҖйӘҢпјҢ然еҗҺеҫ—еҲ°PеҖјпјҢж №жҚ®PеҖјиҝӣиЎҢзӯӣйҖүгҖӮеҚіPеҖји¶Ҡе°ҸпјҢиҜҙжҳҺиҜҘдҪҚзӮ№и¶ҠдёҚз¬ҰеҗҲе“Ҳжё©е№іиЎЎгҖӮ
вқһ
гҖҢдёӨдёӘзӣ®зҡ„пјҡгҖҚ
plink --bfile HapMap_3_r3_8 --hardy plink.hweзҡ„ж•°жҚ®ж јејҸпјҡ
з»“жһңйў„и§Ҳпјҡ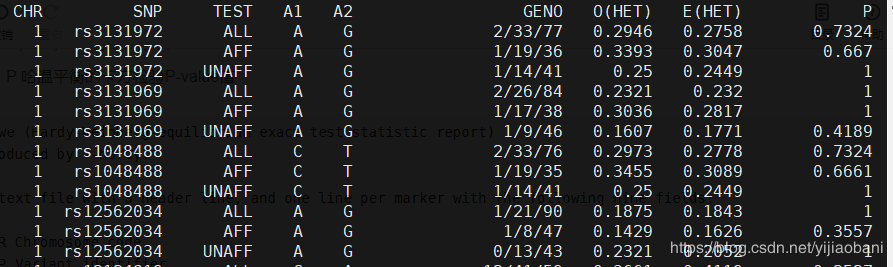
иҝҷйҮҢжҲ‘们дҪҝз”Ёawkпјҡ
awk '{if($9 < 0.0001) print $0}' plink.hwe >plinkzoomhwe.hwe е…ұжңү123дёӘдҪҚзӮ№пјҢе…¶дёӯUNAFFдёә45дёӘдҪҚзӮ№гҖӮ
plink --bfile HapMap_3_r3_8 --hwe 1e-4 --make-bed --out HapMap_3_r3_9
ж—Ҙеҝ—пјҡ
Options in effect:
--bfile HapMap_3_r3_8
--hwe 1e-4
--make-bed
--out HapMap_3_r3_9
515185 MB RAM detected; reserving 257592 MB for main workspace.
1073788 variants loaded from .bim file.
163 people (79 males, 84 females) loaded from .fam.
112 phenotype values loaded from .fam.
Using 1 thread (no multithreaded calculations invoked).
Before main variant filters, 112 founders and 51 nonfounders present.
Calculating allele frequencies... done.
Total genotyping rate is 0.998136.
--hwe: 45 variants removed due to Hardy-Weinberg exact test.
1073743 variants and 163 people pass filters and QC.
Among remaining phenotypes, 56 are cases and 56 are controls. (51 phenotypes
are missing.)
--make-bed to HapMap_3_r3_9.bed + HapMap_3_r3_9.bim + HapMap_3_r3_9.fam ...
done.
еҸҜд»ҘзңӢеҲ°пјҢе…ұжңү45дёӘSNPж №жҚ®е“Ҳжё©зҡ„PеҖјиҝҮж»ӨжҺүдәҶпјҢе’ҢдёҠйқўжүӢеҠЁи®Ўз®—зҡ„дёҖж ·гҖӮ
Rд»Јз Ғпјҡ
hwe<-read.table (file="plink.hwe", header=TRUE)
pdf("histhwe.pdf")
hist(hwe[,9],main="Histogram HWE")
dev.off()
hwe_zoom<-read.table (file="plinkzoomhwe.hwe", header=TRUE)
pdf("histhwe_below_theshold.pdf")
hist(hwe_zoom[,9],main="Histogram HWE: strongly deviating SNPs only")
dev.off()
е“Ҳжё©зҡ„PеҖјзӣҙж–№еӣҫпјҡ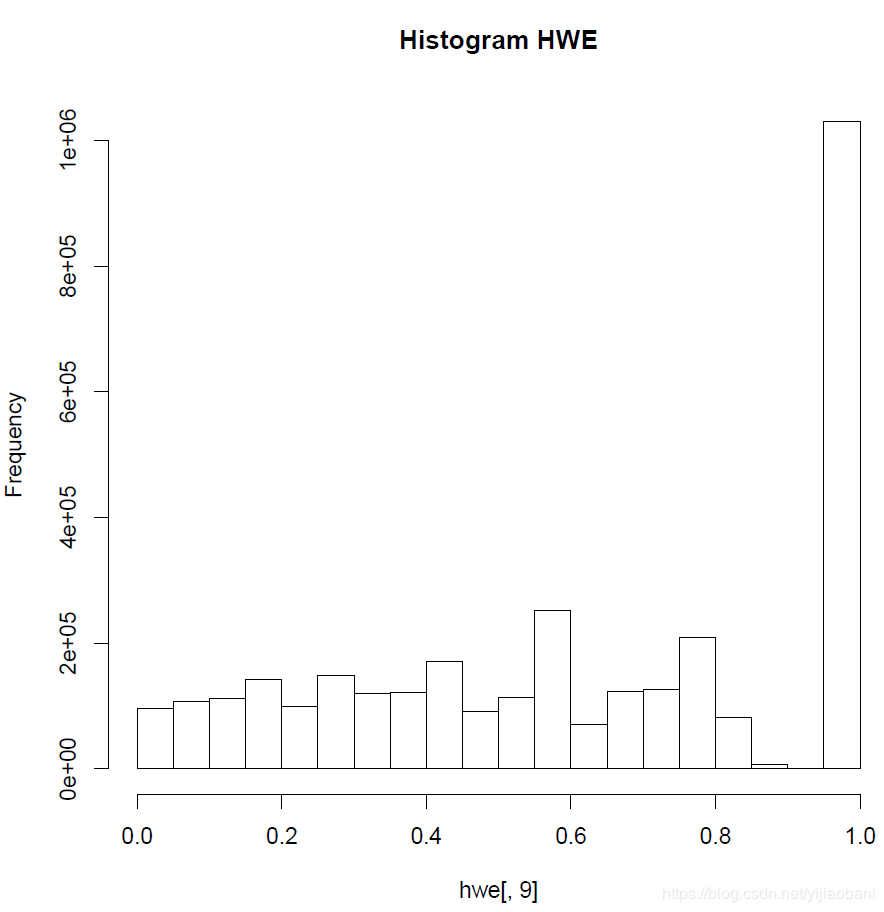
иҝҮж»ӨжҺүSNPдҪҚзӮ№зҡ„PеҖјпјҡ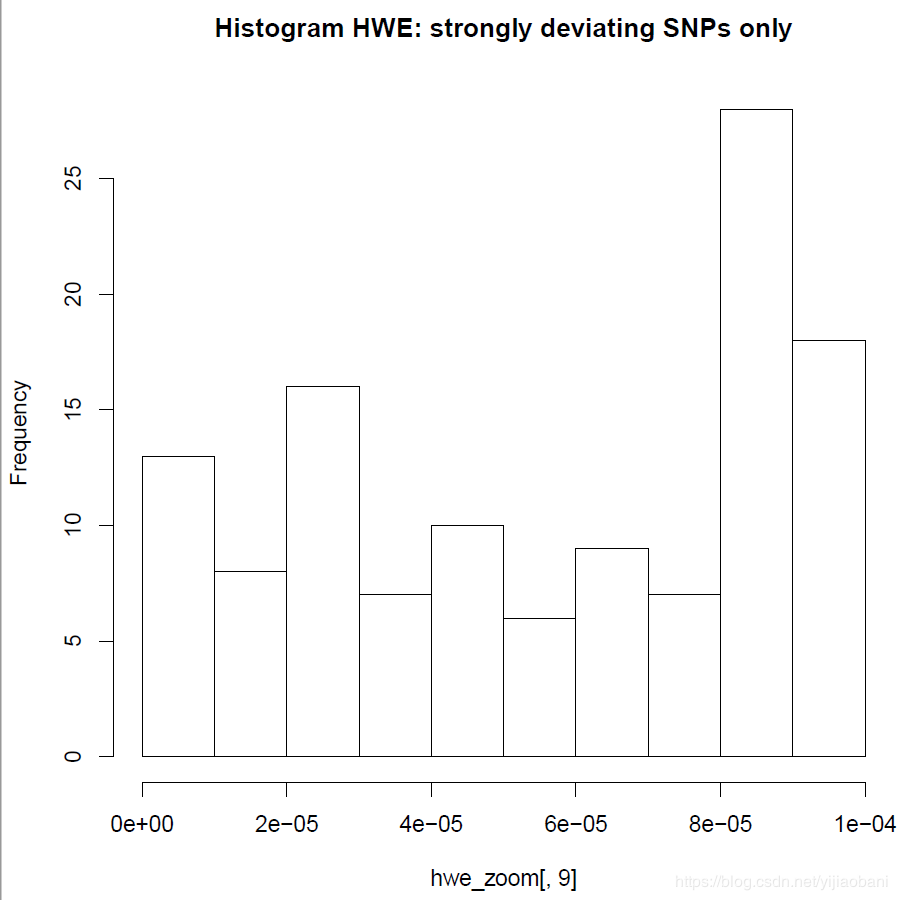
HapMap_3_r3_9.bed HapMap_3_r3_9.bim HapMap_3_r3_9.fam HapMap_3_r3_9.log
е…ідәҺвҖңGWASе“Ҳжё©е№іиЎЎжЈҖйӘҢзҡ„ж–№жі•вҖқиҝҷзҜҮж–Үз« зҡ„еҶ…е®№е°ұд»Ӣз»ҚеҲ°иҝҷйҮҢпјҢж„ҹи°ўеҗ„дҪҚзҡ„йҳ…иҜ»пјҒзӣёдҝЎеӨ§е®¶еҜ№вҖңGWASе“Ҳжё©е№іиЎЎжЈҖйӘҢзҡ„ж–№жі•вҖқзҹҘиҜҶйғҪжңүдёҖе®ҡзҡ„дәҶи§ЈпјҢеӨ§е®¶еҰӮжһңиҝҳжғіеӯҰд№ жӣҙеӨҡзҹҘиҜҶпјҢж¬ўиҝҺе…іжіЁдәҝйҖҹдә‘иЎҢдёҡиө„и®Ҝйў‘йҒ“гҖӮ
е…ҚиҙЈеЈ°жҳҺпјҡжң¬з«ҷеҸ‘еёғзҡ„еҶ…е®№пјҲеӣҫзүҮгҖҒи§Ҷйў‘е’Ңж–Үеӯ—пјүд»ҘеҺҹеҲӣгҖҒиҪ¬иҪҪе’ҢеҲҶдә«дёәдё»пјҢж–Үз« и§ӮзӮ№дёҚд»ЈиЎЁжң¬зҪ‘з«ҷз«ӢеңәпјҢеҰӮжһңж¶үеҸҠдҫөжқғиҜ·иҒ”зі»з«ҷй•ҝйӮ®з®ұпјҡis@yisu.comиҝӣиЎҢдёҫжҠҘпјҢ并жҸҗдҫӣзӣёе…іиҜҒжҚ®пјҢдёҖз»ҸжҹҘе®һпјҢе°Ҷз«ӢеҲ»еҲ йҷӨж¶үе«ҢдҫөжқғеҶ…е®№гҖӮ
жӮЁеҘҪпјҢзҷ»еҪ•еҗҺжүҚиғҪдёӢи®ўеҚ•е“ҰпјҒ